Ligation sequencing DNA V14 (SQK-LSK114) [ライゲーションシークエンシングDNA V14 (SQK-LSK114) ] (GDE_9161_v114_revAC_24Sep2025)
Flongle: Protocol
Ligation sequencing DNA V14 (SQK-LSK114) [ライゲーションシークエンシングDNA V14 (SQK-LSK114) ] V GDE_9161_v114_revAC_24Sep2025
- このプロトコールではゲノムDNAを使用します。
- 調製時間は約60分です。
- フラグメンテーションは任意としています。
- PCR無し
- R10.4.1フローセルとの互換性
研究用のみ
この翻訳は英語バージョン「X」をもとに翻訳されています。 新しいバージョンが出ている可能性があるので、この翻訳を使用する前にコミュニティーで今の英語のバージョンをご確認ください。
FOR RESEARCH USE ONLY
Contents
プロトコールの紹介
ライブラリー調製
シークエンスとデータ解析
トラブルシューティング
概要
- このプロトコールではゲノムDNAを使用します。
- 調製時間は約60分です。
- フラグメンテーションは任意としています。
- PCR無し
- R10.4.1フローセルとの互換性
研究用のみ
この翻訳は英語バージョン「X」をもとに翻訳されています。 新しいバージョンが出ている可能性があるので、この翻訳を使用する前にコミュニティーで今の英語のバージョンをご確認ください。
1. プロトコールの概要
Ligation Sequencing Kit V14 (SQK-LSK114) プロトコルの紹介
このプロトコールは、Ligation Sequencing Kit V14 (SQK-LSK114)を用いたDNAサンプルのシークエンスを行う方法を説明します。この技術に慣れるために、最初にLambdaコントロール実験を行うことを推奨します。
シーケンシングワークフローにおける手順:
実験の準備
実験の前に以下の準備が必要です。
- DNAを抽出し、その長さ、量と純度を確認します。 プロトコル中に実行される品質チェックは実験を成功させるために不可欠です。
- シークエンスキット、適切な装置、およびサードパーティ製試薬が全て揃っていることを確認してください。
- データの取得、および分析するためのソフトウェアをダウンロードしてください。
- フローセルをチェックし、シークエンシングを良好に行うために十分なポアがあることを確認してください。
ライブラリー調製
次の表は、ライブラリー調製手順の概要を示しています。また、オプションで操作を中断できるポイントも示しています。
| ライブラリー調製 | プロセス | 時間 | 停止可能なタイミング(オプション) |
|---|---|---|---|
| DNA修復、およびエンドプレップ | DNAを修復し、DNA末端をアダプターに接続する準備をします。 | 35分 | 4 ° Cで一晩保存 |
| アダプターのライゲーションとクリーンアップ | DNA末端にシークエンスアダプターを取り付けます。 | 20分 | ライブラリーを調製したら、すぐにシークエンスすることを強くお勧めします。 短期間の保管や、フローセルへの再装填など繰り返し使用する場合は、4℃で保管できます。 長期保存、1回使用の場合は-80℃で保存してください。 |
| フローセルのプライミングとローディング | フローセルをプライミングし、調製したライブラリーをシークエンス用にロードします | 5分 |

シークエンシングと解析
実験の事前に以下の手順を行うことが必要です。
- MinKNOWソフトウェアを使用してシークエンスランを開始します。このソフトウェアはデバイスから生データを収集し、リードをベースコールします。
- EPI2MEソフトウェアを起動し、バイオインフォマティクスワークフローを選択してデータを分析します。
プロトコルの互換性
このプロトコルは、以下のものと組み合わせて使用する必要があります。
- Ligation Sequencing Kit V14 (SQK-LSK114)
- Control Expansion (EXP-CTL001)
- Flongle Sequencing Expansion (EXP-FSE002)
- R10.4.1 Flongle Flow Cells (FLO-FLG114)
- MinION Mk1B - MinION Mk1B IT requirements document
- MinION Mk1C - MinION Mk1C IT requirements document
- MinION Mk1D - MinION Mk1D IT requirements document
- GridION - GridION IT requirements document
2. 機器と消耗品
材料
- 500 ng (or 50-100 fmol) of high molecular weight DNA
- OR 50+ ng high molecular weight genomic DNA if performing DNA fragmentation
- Ligation Sequencing Kit V14 (SQK-LSK114)
- Flongle Sequencing Expansion (EXP-FSE002)
消耗品
- Flongle Flow Cell
- Qubit dsDNA HS Assay Kit (Invitrogen, Q32851)
- NEBNext® Companion Module v2、Oxford Nanopore Technologies® Ligation Sequencing用 (NEB, E7672S or E7672L)
- nuclease-free waterで調整した 80% エタノール溶液
- Nuclease-free water (e.g. ThermoFisher, AM9937)
- 1.5 ml Eppendorf DNA LoBind tubes
- 0.2 ml 薄壁のPCRチューブ
- Qubit™ Assay Tubes (Invitrogen, Q32856)
装置
- MinIONかGridION のデバイス
- Flongle adapter
- Hula mixer(緩やかに回転するミキサー)
- 1.5 mlエッペンドルフチューブに最適のマグネット式ラック
- 小型遠心機
- ボルテックスミキサー
- サーマルサイクラー
- P1000 ピペット及びチップ
- P200 ピペットとチップ
- P100 ピペットとチップ
- P20 ピペットとチップ
- P10 ピペットとチップ
- P2 ピペットとチップ
- アイスバケツ(氷入り)
- タイマー
- Qubit蛍光光度計(またはQCチェックのための同等品)
フローセルの劣化/飽和状態
オックスフォード・ナノポアでは、より堅牢な製品をお届けするために、製造プロセスの継続的な改善に取り組んでいます。Flongleの場合、出荷するフローセルの安定性は向上しています。しかし、少数のフローセルでは、フローセルに負荷をかけると、フローセルが急速に劣化してしまいます。これはMinKNOW GUIでsaurationとして見ることができます。弊社では、この問題を解決するために努力しておりますが、その間に、以下のようなローディングを推奨し、Flongleフローセルに同梱されているFlongle Sequencing Expansion (EXP-FSE002)のバッファーを使用することをお勧めします。もしフローセルが急速に劣化/飽和した場合は、support@nanoporetech.com。
ロードに関する推奨事項 標準的なインプットの推奨に従って、このプロトコールは少なくとも2つのFlongleフローセルにロードするのに十分な最終ライブラリー(EB中の適合DNA)を生産するはずです。2台目のFlongleフローセルからより多くのデータを得る必要がある場合は、2台目のFlongleフローセルをロードするのに十分なライブラリーを確保しておくことを推奨します。
ローディング時にフローセルに直接接触するバッファーは3種類あります(SB: Sequencing Buffer、FCF: Flow Cell Flush、LIB: Library BeadsまたはLIS: Library Solution)。これらのバッファーを調べたところ、プラスチックバイアルから染み出す汚染物質が非常に少なく、Flongleフローセルシステムの堅牢性に影響を与えることがわかりました(MinIONとPromethIONはこの影響を受けません)。
これらのバッファーをプラスチック製ではなくガラス製バイアルで保管すると、劣化の発生率が減少することがわかりました。

Flongleユーザーへの迅速な展開のため、これら3つのコンポーネントをガラスバイアルに入れたFlongle Sequencing Expansion (EXP-FSE002)を作製しました。
Flongleフローセルにライブラリーをロードするには、以下のコンポーネントが必要です:
**Flongle Sequencing Expansion (EXP-FSE002) コンポーネント **
- Sequencing Buffer (SB)
- Flow Cell Flush (FCF)
- Library Beads (LIB) 又は Library Solution (LIS)
Sequencing Kit コンポーネント
- Flow Cell Tether (FCT)
Oxford Nanopore Technologies は、フローセルエクスパンションの耐用期間をお客様の受領後6ヶ月とみなします。
インプットDNA
インプットDNAのQC方法
インプットDNAの量と品質の要件を満たすことが重要です。DNAの使用量が少なすぎたり多すぎたり、あるいは品質の低いDNA(例としてDNAが非常に断片化されていたり、RNAや化学汚染物質が含まれている場合など)を使用すると、ライブラリーの調製に影響を及ぼす可能性があります。
DNAサンプルの品質管理の方法については、Input DNA/RNA QC protocolのプロトコルをご覧ください。
コンタミネーション
DNAの抽出する方法によっては、精製DNAに特定の化学汚染物質が残留する可能性があり、ライブラリ調製の効率やシークエンシングの品質に影響を及ぼす可能性があります。コンタミネーションについての詳細は、コミュニティーの Contaminants page をご覧ください。
Oxford Nanopore Technologies® Ligation Sequencing用のNEBNext® Companion Module v2
NEBNext® Companion Module v2 for Oxford Nanopore Technologies® Ligation Sequencing (catalogue number E7672S or E7672L), を購入されることをお勧めします。この商品にはLigation Sequencing Kitで使用するために必要なすべてのNEB試薬が含まれています。
旧バージョンのNEBNext® Companion Module for Oxford Nanopore Technologies® Ligation Sequencing (NEB, E7180S or E7180L)と互換性がありますが、新しい「モジュールv2」では、FFPEv2 DNA Repair BufferとSalt-T4 DNA Ligaseにより、より効率的なdA-tailingとligationが可能になりました。v2モジュールを使用すると、サンプルあたりのコストを削減できます。
(注: アンプリコンのプロトコールについては、NEBNext FFPE DNA Repair Mixをお買い求めいただくことも可能ですが、試薬を別途でお買い求めいただく方がコスト的に有利です。
サードパーティー試薬
このプロトコールで使用されているすべてのサードパーティー試薬は、当社が検証し、使用を推奨しているものです。Oxford Nanopore Technologiesでは、それ以外の試薬を用いたテストは行っていません。
すべてのサードパーティ製試薬については、製造元の指示に従って使用の準備をすることをお勧めします。
フローセルのチェックをしてください
シークエンシング実験を開始する前に、フローセルのポアの数を確認することを強くお勧めします。このフローセルの確認は、MinION/GridION/PromethIONの場合は代理店への到着から12週間以内に行ってください。またはFlongle Flow Cellの場合は代理店への到着から4週間以内に行う必要があります。Oxford Nanopore Technologiesは、フローセルチェックの実施から2日以内に結果が報告され、推奨される保管方法に従っていた場合に、以下の表に記載されているナノポアの有効数に満たさない場合には、フローセルを交換します。 フローセルのチェックを行うには、Flow Cell Check documentの指示に従ってください。
| Flow cell | 保証する最小有効ポア数(以下の数未満のフローセルが交換対象となります) |
|---|---|
| Flongle Flow Cell | 50 |
| MinION/GridION Flow Cell | 800 |
| PromethION Flow Cell | 5000 |
ライゲーションアダプター(LA)のライゲーション効率を高めるため、NEBNext Quick Ligation Module に付属しているリガーゼバッファーではなく、Ligation Sequencing Kit V14 に付属のライゲーションバッファー(LNB)のご使用を強くお勧めします。
本キットおよびプロトコールに含まれるライゲーションアダプター(LA)は、他のシークエンシングアダプターとの互換性はありません。
Ligation Sequencing Kit V14 (SQK-LSK114) のコンテンツ
(注: 現在のキットの容器を変更しています。今までは実験毎に使い捨てのシングルユーズチューブを使用していましたが、バッファー単位のボトル容器に変更しています。
シングルユースチューブの場合:
ボトル容器の場合:
(注: 本製品には、Beckman Coulter、Inc.製のAMPure XP試薬が含まれており、試薬の安定性を損なうことなくキットと共に-20 ° Cで保存することができます。
(注: DNA Control Sample(DCS)は3.6kbのアンプリコンで、Lambda genomeの3'末端をマッピングしたプレップコントロールです。
Flongle Sequencing Expansion (EXP-FSE002) 内容物
| 名称 | 頭字語 | キャップの色 | バイアルの数 | 1バイアルあたりの容量 (µl) |
|---|---|---|---|---|
| Sequencing Buffer | SB | Blue | 1 | 250 |
| Library Beads | LIB | Blue | 1 | 200 |
| Library Solution | LIS | Blue | 1 | 200 |
| Flow Cell Flush | FCF | Blue | 1 | 1,600 |
オックスフォード・ナノポア・テクノロジーは、Flow Cell Expansion の耐用期間を、お客様による受領から6ヶ月間とみなします。
オックスフォード・ナノポア・テクノロジーズは、Flongle Sequencing Expansion (EXP-FSE002)の耐用期間をお客様の受領から6ヶ月間と見なしています。
3. DNA修復およびエンドプレップ
材料
- 500 ng 高分子量ゲノムDNA / 50-100 fmol アンプリコンDNA
- DNA Control Sample (DCS)
- AMPure XP Beads (AXP)
消耗品
- NEBNext® FFPE DNA Repair Mix (M6630) from the NEBNext® Companion Module v2 (NEB, E7672S or E7672L)
- NEBNext® Ultra II End Prep Enzyme Mix (E7646) from the NEBNext® Companion Module v2 (NEB, E7672S or E7672L)
- NEBNext® FFPE DNA Repair Buffer v2 (E7363) from the NEBNext® Companion Module v2 (NEB, E7672S or E7672L)
- Qubit dsDNA HS Assay Kit (Invitrogen, Q32851)
- nuclease-free waterで調整した 80% エタノール溶液
- Nuclease-free water (e.g. ThermoFisher, AM9937)
- Qubit™ Assay Tubes (Invitrogen, Q32856)
- 1.5 ml Eppendorf DNA LoBind tubes
- 0.2 ml 薄壁のPCRチューブ
装置
- P1000 ピペット及びチップ
- P100 ピペットとチップ
- P10 ピペットとチップ
- サーマルサイクラー
- 小型遠心機
- Hula mixer(緩やかに回転するミキサー)
- マグネットラック
- アイスバケツ(氷入り)
- Qubit蛍光光度計(またはQCチェックのための同等品)
NEB試薬がすべて含まれていまれている Oxford Nanopore Technologies® Ligation Sequencing (catalogue number E7672Sまたは、 E7672L)用のNEBNext® Companion Module v2)を使用する事をお勧めします。
旧バージョンのNEBNext® Companion Module for Oxford Nanopore Technologies® Ligation Sequencing (NEB, E7180S or E7180L)も使用可能です。しかし、上記で推奨したv2モジュールを使用する事でより効率的なdA-tailingとligationを提供できます。
フローセルのチェックを行ってください。
ライブラリー調製を開始する前にフローセルチェックを行い、良好なシークエンスランに十分なポアを持つフローセルを使用することをお勧めします。
詳細については、MinKNOWプロトコルのflow cell check instructions を参照してください。
DNA Control Sample(DCS)を室温で融解し、スピンダウンしてピペッティングで混合し、氷上に置きます。
NEB試薬を製造元の指示に従って調製し、氷上に置きます。
最適なパフォーマンスを得るために、NEBは以下を推奨しています。
すべての試薬を氷上で解凍します。
試薬チューブをタッピングや転倒混和にてよく混ぜてください。
(注: FFPE DNA Repair MixまたはUltra II End Prep Enzyme Mixをボルテックスしないでください。毎日、初めて開封する前に、必ずチューブをスピンダウンしてください。
FFPE DNA Repair Buffer v2、または NEBNext FFPE DNA Repair Buffer と Ultra II End Prep Reaction Buffer をボルテックスし、よく混合してください。
(注: これらのバッファーは白色の沈殿を含むことがあります。このような場合には混合物を室温で戻し、バッファー液を数回上下にピペットで沈殿物を分解してください。その後、素早くチューブをボルテックスして混合させてください。FFPE DNA Repair Bufferは黄色味を帯びることがありますが、問題はありません。
ヌクレアーゼを含まない水でDNAを調製します
- 500ng(または50-100fmol)のインプットDNAを1.5mlのEppendorf DNA LoBindチューブに移します。
- ヌクレアーゼを含まない水で容量を23.5μlに調整します。
- 不要なシャーリングを避けるため、チューブをはじきながら十分に混合します。
- マイクロフュージで短時間スピンダウンします。
0.2mlの薄壁PCRチューブに以下のものを入れて混合します
それぞれのステップの間に、ピペットで10-20回混ぜます。
| 試薬 | 容量 |
|---|---|
| DNA from the previous step | 23.5 µl |
| DNA CS (optional) | 0.5 µl |
| NEBNext FFPE DNA Repair Buffer v2 | 3.5 µl |
| NEBNext FFPE DNA Repair Mix | 1 µl |
| Ultra II End-prep Enzyme Mix | 1.5 µl |
| 合計 | 30 µl |
旧バージョンのNEBNext® Companion Module for Oxford Nanopore Technologies® Ligation Sequencing(NEB、E7180SまたはE7180L)をご使用の場合:
それぞれのステップの間に、ピペットで10~20回混ぜます
| 試薬 | 容量 |
|---|---|
| DCS | 0.5 µl |
| DNA | 23.5 µl |
| NEBNext FFPE DNA Repair Buffer | 1.75 µl |
| NEBNext FFPE DNA Repair Mix | 1 µl |
| Ultra II End-prep Reaction Buffer | 1.75 µl |
| Ultra II End-prep Enzyme Mix | 1.5 µl |
| 合計 | 30 µl |
反応液を完全に混合するために、ゆっくりとピペッティングし短時間スピンダウンして下さい。
サーマルサイクラーを使用して、初めに20℃で5分間インキュベートした後に、65℃で5分間インキュベートしてください。
AMPure XP ビーズ(AXP)をボルテックスで懸濁します。
DNA サンプルを清潔な 1.5 ml エッペンドルフ DNA LoBind チューブに移してください。
再懸濁したAMPure XPビーズ(AXP)30 µlをエンドプレップ反応に加え、チューブをはじくように混ぜます。
Hula mixer(緩やかに回転するミキサー)で5分間インキュベートします(常温)。
新鮮な80%エタノールをヌクレアーゼフリー水で500μl用意します。
チューブをスピンダウンした後、マグネットラック上で、上清が無色透明になるまで置きます。チューブを磁石の上に置いたまま、上清をピペットで取り除いていきます。ピペットを使用してエタノールを除去し 、 廃棄してください。
チューブをマグネットの上に置き、ペレットを乱さないように、200 µl の新しく調製した 80% エタノールでビーズを洗浄します。
前のステップを繰り返します。
スピンダウンし、チューブをマグネットの上に戻します。残ったエタノールをピペットで取り除きます。ペレットを30 秒間程乾かします。 ただし、 ペレットにひびが入るまでは乾燥させないでください。
チューブをマグネットラックから取り出し、ペレットを31 µlの無核水に懸濁します。その後、室温で2分間インキュベートします。
溶出液が無色透明になるまで、少なくとも1分間マグネット上でビーズをペレット化します。
31 µl の溶出液を除去し、1.5 ml エッペンドルフ DNA LoBind チューブに入れます。
Qubit蛍光光度計を使用して、溶出したサンプル1 µlを定量します。
エンドプレップと修復されたDNAをアダプターライゲーションのステップに進めます。なお、この時点でサンプルを4℃で一晩保存することも可能です。
4. アダプターのライゲーションとクリーンアップ
材料
- Ligation Adapter (LA)
- Ligation Buffer (LNB)
- Long Fragment Buffer (LFB)
- Short Fragment Buffer (SFB)
- AMPure XP Beads (AXP)
- Elution Buffer (EB)
消耗品
- Salt-T4® DNA Ligase (NEB, M0467)
- Qubit dsDNA HS Assay Kit (Invitrogen, Q32851)
- Qubit™ Assay Tubes (Invitrogen, Q32856)
- 1.5 ml Eppendorf DNA LoBind tubes
装置
- マグネットラック
- 小型遠心機
- ボルテックスミキサー
- P1000 ピペット及びチップ
- P100 ピペットとチップ
- P20 ピペットとチップ
- P10 ピペットとチップ
- Qubit蛍光光度計(またはQCチェックのための同等品)
Salt-T4® DNA Ligase (NEB, M0467) の使用を推奨します。
Salt-T4® DNA Ligase(NEB, M0467)は別途購入するか、Oxford Nanopore Technologies® Ligation Sequencing用のNEBNext® Companion Module v2(カタログ番号E7672SまたはE7672L)に含まれています。
旧バージョンのNEBNext® Companion Module for Oxford Nanopore Technologies® Ligation Sequencing (NEB, E7180S or E7180L)も使用することが出来ます。しかし、上記で推奨したv2モジュールを使用する事でより効率的なdA-tailingとligationを提供することが出来ます。
推奨の他社製リガーゼ(ligase)には専用のバッファーが付属していますが、Ligation Sequencing Kitに付属のLigation Buffer (LNB)を使用した方が、Ligation Adapter (LA)のライゲーション効率が高くなります。
Ligation Adapter (LA) とSalt-T4® DNA Ligaseをスピンダウンし、氷上に置きます。
ライゲーションバッファー(LNB)を室温で融解し、スピンダウンしてピペッティングで混合します。粘性が高い為、この緩衝液をボルテックスするのは効果的ではないです。解凍して混ぜたら、すぐに氷の上に置いてください。
溶出バッファー(EB)を室温で融解し、ボルテックスで混合します。その後、スピンダウンして氷の上に置きます。
使用するウォッシュバッファー(LFBまたはSFB)に応じて、アダプターライゲーション後のクリーンアップステップは、3 kb以上のDNAの断片を濃縮するか、全ての断片長を均等に精製するように設計されています。
- 3kb以上のDNA断片を濃縮するには、Long Fragment Buffer (LFB)を使用してください。
- 一方であらゆるサイズの DNA 断片を保持するには、Short Fragment Buffer (SFB) を使用してください。
Long Fragment Buffer(LFB)または Short Fragment Buffer(SFB)のいずれかを室温で解凍し、ボルテックスで混合します。その後、スピンダウンして氷の上に置きます。
1.5mlのエッペンドルフDNA LoBindチューブに、以下の順序で混合します
それぞれの追加の合間に、10~20回ピペットミックスをして下さい。
| 試薬 | 量 |
|---|---|
| 前ステップのDNAサンプル | 30 µl |
| Ligation Adapter (LA) | 2.5 µl |
| Ligation Buffer (LNB) | 12.5 µl |
| Salt-T4® DNA Ligase | 5 µl |
| 合計 | 50 µl |
反応液を完全に混合するために、ゆっくりとピペッティングし短時間スピンダウンして下さい。
反応液を室温で10分間インキュベートします。
AMPure XP ビーズ(AXP)をボルテックスで懸濁します。
再懸濁したAMPure XPビーズ(AXP)20μlを反応液に加え、チューブをはじくように混ぜます。
Hula mixer(緩やかに回転するミキサー)で5分間インキュベートします(常温)。
サンプルをスピンダウンし、マグネット上でペレット化します。チューブをマグネットの上に置き、無色透明になったら上清をピペットで取り除きます。
125μl Long Fragment Buffer(LFB)または125μl Short Fragment Buffer(SFB)を加えてビーズを洗浄する。ビーズをフリックして再懸濁し、チューブをマグネットラックに戻し、ビーズをペレット化する。ピペットで上清を取り除き、廃棄する。
前のステップを繰り返します。
スピンダウンし、チューブをマグネットの上に戻します。残った上清をピペットで取り除きます。ペレットを30 秒間程乾かします。 ただし、 ペレットにひびが入るまでは乾燥させないでください。
チューブをマグネットラックから取り出し、ペレットを 7 µl Elution Buffer (EB)に懸濁します。室温で10分間インキュベートします。高分子DNAの場合、37℃でインキュベートすると、長い断片の回収率が向上します。
溶出液が無色透明になるまで、少なくとも1分間マグネット上でビーズをペレット化します。
DNA ライブラリーを含む溶出液 7 µl を取り出し、1.5 ml エッペンドルフ DNA LoBind チューブに入れる。
ペレット化したビーズを廃棄します
Qubit蛍光光度計を使用して、溶出したサンプル1 µlを定量します。
最終ライブラリーを5~10fmolになるように、5μlのElution Buffer(EB)で調製します。
必要であれば、NEB calculatorのような質量-mol計算機を使用することを推奨します。
R10.4.1フローセルに、この最終調製ライブラリーを5-10fmolロードすることを推奨する。
標準的なインプットの推奨に従って、このプロトコールは少なくとも2つのFlongleフローセルにロードするのに十分な最終ライブラリー(EB中のアダプターDNA)を生産するはずです。2つ目のフローセルにロードするのに十分なライブラリーを確保しておくことを推奨します。10fmol以上の負荷は出力に悪影響を及ぼす可能性があります。ライブラリーをEBまたはヌクレアーゼフリー水で最終容量5μlに希釈する。
調製されたライブラリーは、フローセルへのロードに使用されます。ライブラリーは、ロードの準備ができるまで氷上、または4℃で保存して下さい。
推奨のライブラリー保存方法
短期間の保存や繰り返し使用する場合は(例 フローセルをウオッシュして再度ロードする場合)は、ライブラリーをEppendorf DNA LoBindチューブに入れ、4℃で保存 することをお勧めします。 __3か月以上の長期保存の場合は、____ライブラリーをEppendorf DNA LoBindチューブに -80 ° Cで保存 することをお勧めします。
5. Flongle Flow Cellのローディング
材料
- Flongle Sequencing Expansion (EXP-FSE002)
- Flow Cell Tether (FCT)
消耗品
- Flongle Flow Cell
- 1.5 ml Eppendorf DNA LoBind tubes
装置
- Flongle adapter
- MinIONかGridION のデバイス
- P200 ピペットとチップ
- P20 ピペットとチップ
- P10 ピペットとチップ
このキットはR10.4.1フローセル(FLO-FLG114)のみに対応しています。
ローディング時にフローセルに直接接触するバッファーは3種類あります(SB: Sequencing Buffer、FCF: Flow Cell Flush、LIB: Library BeadsまたはLIS: Library Solution)。これらのバッファーを調べたところ、プラスチックバイアルから染み出す汚染物質が非常に少なく、Flongleフローセルシステムの堅牢性に影響を与えることがわかりました(MinIONとPromethIONはこの影響を受けません)。
これらのバッファーをプラスチック製ではなくガラス製バイアルで保管すると、劣化の発生率が減少することがわかりました。

Flongleユーザーへの迅速な展開のため、これら3つのコンポーネントをガラスバイアルに入れたFlongle Sequencing Expansion (EXP-FSE002)を作製しました。
Flongleフローセルにライブラリーをロードするには、以下のコンポーネントが必要です:
**Flongle Sequencing Expansion (EXP-FSE002) コンポーネント **
- Sequencing Buffer (SB)
- Flow Cell Flush (FCF)
- Library Beads (LIB) 又は Library Solution (LIS)
Sequencing Kit コンポーネント
- Flow Cell Tether (FCT)
Oxford Nanopore Technologies は、フローセルエクスパンションの耐用期間をお客様の受領後6ヶ月とみなします。
Flongleフローセルアレイの裏面やFlongleアダプターのコンタクトパッドには触れないでください。フローセルやアダプターの破損を防ぐため、フローセルやアダプターを取り扱う際は必ず手袋を着用してください。
下図はFlongleフローセルの構成部品を示しています
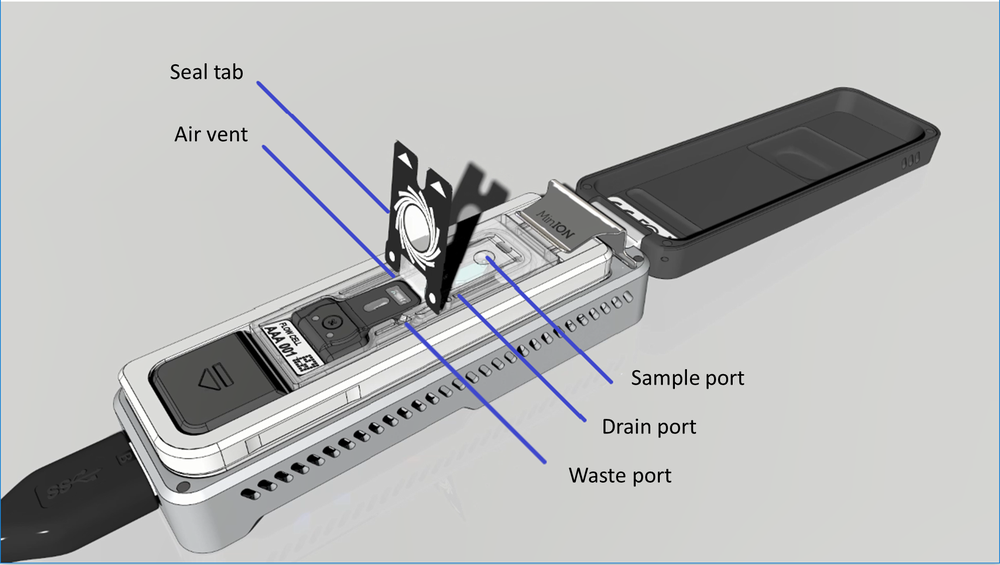
シールタブ、エアベント、ウェイストチャンネル、ドレンポート、サンプルポートがここに見えます。サンプルポート、ドレインポート、エアベントは、シールタブを剥がして初めてアクセスできるようになります。
Sequencing Buffer(SB)、Library Beads(LIB)またはLibrary Solution(LISを使用する場合のみ)、Flow Cell Tether(FCT)およびFlow Cell Flush(FCF)を室温で融解してから、ボルテックスで混合します。その後、スピンダウンして氷上で保存します。
新しい1.5 mlエッペンドルフDNA LoBindチューブに、117 µlのFlow Cell Flush (FCF) と3 µlのFlow Cell Tether (FCT)を入れ、ピペットで混ぜる。
FlongleアダプターをMinIONまたは5つのGridIONポジションのいずれかにセットする。
アダプターはMinION Mk1BまたはGridIONプラットフォー ム上に均等に平らに置く。こうすることで、次のステージでフローセルアセンブリーが平坦になります。
Flongleフローセルを挿入する前に、アダプターをデバイスに接続し、デバイスの電源を入れる必要があります。

フローセルをFlongleアダプターにセットし、カチッと音がするまでフローセルを押し下げます。
フローセルは、流体コンパートメント内に気泡が生じないよう、アダプター内に均等かつ平坦に設置する。

Flongleフローセルのプライミングとロード方法
サンプルポートが見える位置まで、Flongleフローセルからシールタブを以下のように剥がしてください
- シールタブを持ち上げます:
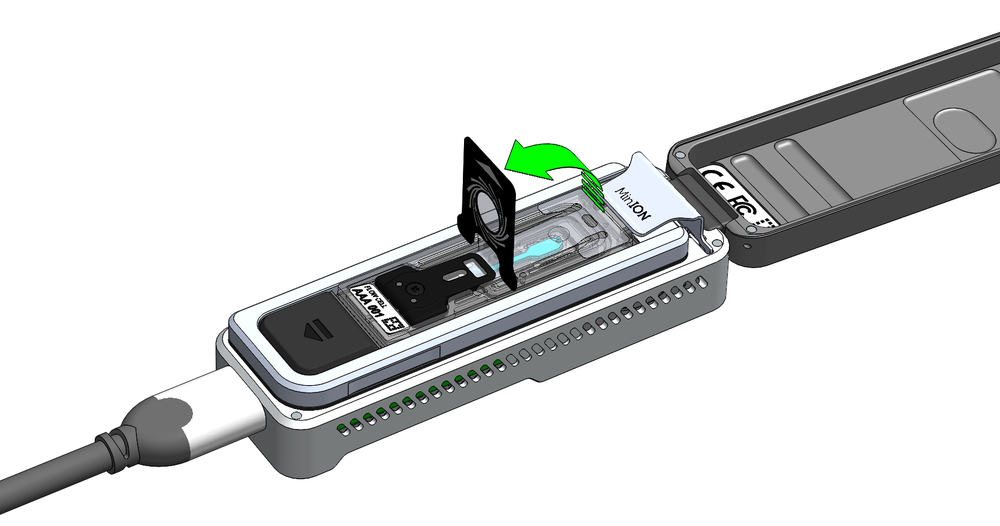
- シールタブを引き、サンプル・ポートにアクセスします。

- シールタブの粘着剤をMinION Mk 1Bの蓋に貼り付けて、シールタブを開いたままにします。

先に調製したFlow Cell Flush(FCF)とFlow Cell Tether (FCT)の混合液でフローセルをプライミングするには、サンプルポートやピペットチップにエアギャップがないことを確認します。P200ピペットチップをサンプルポートにセットし、120µlのプライミング液をゆっくりとピペッ トしてFlongleフローセルに分注します。フローセルを勢いよく流しすぎないよう、ピペットのプランジャーをひねりながら押し下げることもお勧めします。

Library Beads(LIB)チューブにはビーズの懸濁液が入っています。これらのビーズはすぐに沈殿するので、使用直前に混合することが重要です。
ほとんどのシーケンス実験にはLibrary Beads (LIB)の使用を推奨します。しかし、より粘性の高いライブラリーにはLibrary Solution(LIS)を使ってください。
Library Beads(LIB)のバイアルをボルテックスする。ビーズはすぐに沈殿するので、すぐに新しい1.5mlのエッペンドルフDNA LoBindチューブにSequencing Mixを以下のように準備し、Flongleにロードする。
| 試薬 | 量 |
|---|---|
| Sequencing Buffer (SB) | 15 µl |
| Library Beads (LIB)は使用直前に混合し使用するか、Library Solution (LIS)を使用してください。 | 10 µl |
| DNA library | 5 µl |
| 合計 | 30 µl |
シーケンスミックスをフローセルに添加するには、サンプルポートやピペットチップにエアギャップがないことを確認してください。P200チップをサンプルポート内に置き、ゆっくりとピペッティングしてSequencing Mixをフローセルに分注します。フローセルを勢いよく流しすぎないよう、ピペットのプランジャーをひねりながら押し下げることもお勧めします。

Flongleフローセルをシールタブの接着剤で以下のようにシールする:
- 透明粘着テープをサンプルポートに貼り付けます

- シールタブの上部(ホイールアイコン部)を元の位置に戻します。

デバイスの蓋を閉め、MinKNOWでシークエンスランをセットします。
When a flow cell is inserted into the MinION Mk1D, the device lid will sit on top of the flow cell, leaving a small gap around the sides. This is normal and has no impact on the performance of the device.
Please refer to this FAQ regarding the device lid.

6. データ収集とベースコール
フローセルをロードしたら、MinKNOWでシーケンスランを開始できます。MinKNOWは、デバイス、データ収集、リアルタイムベースコールを制御するシーケンスソフトウェアです。 MinKNOWのセットアップと使用に関する詳細情報は、MinKNOW protocolをご覧ください。
MinKNOWは、複数の方法でシーケンスに使用し、設定することができます。
- シーケンシングデバイスに直接またはリモートで接続されたコンピューター。
- GridIONまたはPromethION 24/48シーケンスデバイス上で直接使用。
シーケンス機器でのMinKNOWの使用に関する詳細は、各機器のユーザーマニュアルをご覧ください
MinKNOWでシーケンスランを開始します。
1. スタートページに移動し、 Start sequencing. をクリックします。 
2. 実験名、フローセルの位置、サンプルIDなど、実験の詳細を記入します。 
3. キットページで ライブラリー調製に使用するシーケンスキット を選択します。 
4. RunオプションとAnalysisのタブで、シーケンシングパラメーターを設定するか、デフォルト設定のままにします。
注:) シーケンスランのセットアップ時にベースコールがオフになっている場合、ベースコールはMinKNOW上でポストランで実行できます。詳細については、MinKNOW protocolをご覧ください。
5. 出力ページで、出力パラメーターを設定するか、デフォルト設定のままにします。 
6. Reviewページで Start をクリックし、シーケンスランを開始します。 
シーケンシング後のデータ解析
シーケンシングとベースコール後、データを解析することができます。ベースコールおよびベースコール後の解析オプションの詳細については、Data Analysis ドキュメントを参照してください。
ダウンストリーム解析のセクションでは、データを解析するためのさらなるオプションについて概説しています。
7. ダウンストリーム解析
ベースコール後の分析
ベースコールされたデータをさらに解析するには、いくつかの方法があります。
1. EPI2ME workflows
詳細なデータ解析のために、オックスフォード・ナノポア・テクノロジーズは、EPI2MEで利用可能な様々なバイオインフォマティクスのチュートリアルとワークフローを提供しています。このプラットフォームでは、研究チームとアプリケーションチームがGitHubに保存しているワークフローを記載しています。このプラットフォーム内にはバイオインフォマティクスのコードと説明をしているコメント、およびサンプルデータを使ってコードを試すことが出来ます。
2. 研究分析ツール
Oxford Nanopore Technologiesの研究部門では、Oxford Nanopore GitHub repositoryで多数の分析ツールを公開しています。これらのツールは上級ユーザー向けであり、ソフトウェアのインストールと実行方法の説明が含まれています。これらのツールは最低限のサポートしかしていません。
3. コミュニティーで開発されたツール
研究課題に適したデータ解析方法が上記のリソースのいずれにも記載されていない場合は、 resource centre を参照し、アプリケーションに適したバイオインフォマティクスツールを検索してください。 Nanoporeコミュニティーの多くのメンバーが、 ナノポアシークエンシングデータを解析するための独自のツールやパイプラインを開発しており、そのほとんどはGitHubで利用可能です。これらのツールはOxford Nanopore Technologiesではサポート対象外であり、最新のケミストリーやソフトウェア構成との互換性を保証するものではありませんのでご了承ください。
8. DNA/RNA抽出、およびライブラリ調製時の問題点
以下は、最もよく起こる問題のリストであり、いくつかの原因と解決策が提案されています。
Nanopore Community Support セクションにFAQをご用意しています。
ご提案された解決策を試しても問題が解決しない場合は、テクニカルサポートに電子メール (support@nanoporetech.com)または LiveChat in the Nanopore Communityでご連絡ください。
サンプルの品質が低い
| 問題点 | この問題が生じた可能性のある原因 | 解決策とコメント |
|---|---|---|
| DNAの純度が低い(DNAのOD 260/280のナノドロップ測定値が1.8未満およびOD 260/230が2.0~2.2未満) | DNA抽出で必要な純度が得られていない | 夾雑物の影響は、 Contaminants に示されています。コンタミネーションをもたらさないために別の抽出方法extraction method をお試しください。. 追加のSPRIクリーンアップステップの実施を検討して下さい。 |
| 低いRNA インテグリティー(RNA Integrity Number: <9.5 RIN、またはrRNAバンドがゲル上でスメアになっている) | 抽出中にRNAが分解された | 別のRNA抽出方法 RNA extraction methodを試してください。RINの詳細については、 RNA Integrity Number の資料を参照してください。詳細については、 DNA/RNA Handling のページをご覧ください。 |
| RNAのフラグメントが予想より短い | 抽出中にRNAが分解された | 別のRNA抽出方法 RNA extraction methodを試してください。 RINの詳細については、 RNA Integrity Number の資料を参照してください。詳細については、DNA/RNA Handling のページをご覧ください。 RNAを扱う際には、RNaseフリーの環境で作業し、実験器具もRNaseフリーにしておくことをお勧めします。 |
AMPureビーズクリーンアップ後のDNA回収率が低い
| 問題点 | この問題が生じた可能性のある原因 | 解決策とコメント |
|---|---|---|
| 低回収率 | AMPureビーズとサンプルの比率が予想していたのよりも低いことによるDNAの損失 | 1. AMPureビーズはすぐに沈降するため、サンプルに添加する前によく再懸濁させてください。 2. AMPureビーズ対サンプル比が0.4:1未満の場合、どのようなサイズのDNA断片でもクリーンアップ中に失われます。 |
| 低回収率 | DNA断片が予想よりも短い | サンプルに対するAMPureビーズの比率が低いほど、短い断片に対する選択が厳しくなります。 アガロースゲル(または他のゲル電気泳動法)上でインプットDNAの長さを設定してから、使用するAMPureビーズの適切な量を計算してください。 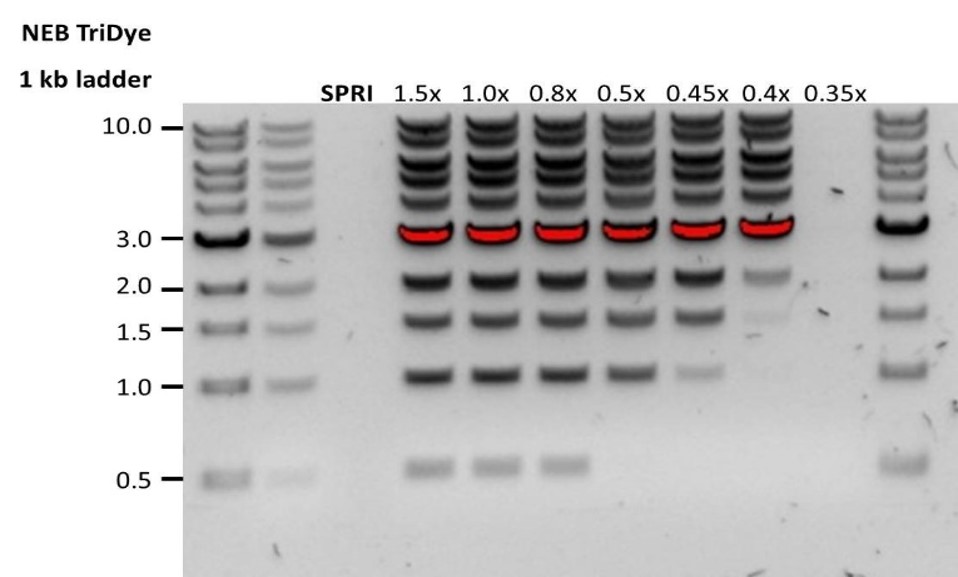 |
| エンドプレップ後の収率が低い | 洗浄ステップで使用したエタノール濃度が低い(70%未満)。 | エタノールが70%未満の場合、DNAは洗浄中にビーズから溶出されます。必ず正しい濃度(%)のエタノールを使用してください。 |
9. シークエンス実行中の問題
以下は、最もよく起こる問題のリストであり、いくつかの原因と解決策が提案されています。
Nanopore Community Support セクションにFAQをご用意しています。
ご提案された解決策を試しても問題が解決しない場合は、テクニカルサポートに電子メール (support@nanoporetech.com)または LiveChat in the Nanopore Communityでご連絡ください。
シークエンス開始時のポアがフローセルチェック後よりも少ない場合
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
| MinKNOWのフローセルチェックで確認されたポアの数より、シークエンシング開始時のポア数が少なく表示された。 | ナノポアアレイに気泡が入ってしまった。 | フローセルチェックをした後、フローセルをプライミングする前に、プライミングポート付近の気泡を取り除くことが必要です。 気泡を取り除かないと、気泡がナノポアアレイに移動し、空気に触れたたナノポアが不可逆的なダメージを負った可能性がある。これを防ぐための最適な方法が、 this videoで紹介されています。 |
| MinKNOWのフローセルチェックで確認されたポアの数より、シークエンシング開始時のポア数が少なく表示された。 | フローセルがデバイスに正しく挿入されていない。 | シークエンスランを停止し、フローセルをシークエンス装置から取り出します。次に再度フローセルを挿入し、装置にしっかりと固定され、目標温度に達していることを確認します。GridIONやPromethIONの場合は別のフローセルの位置をお試しください。 |
| MinKNOWのフローセルチェックで確認されたポアの数より、シークエンシング開始時のポア数が少なく表示された。 | ライブラリー内の汚染物質がポアを失活させたり塞いだりしている。 | フローセルチェックの際のポア数は、フローセル保存バッファー中のQC用のDNA分子を用いて計測されます。シークエンシングの開始時は、ライブラリ自体を使用してアクティブなポア数を推定します。このため、フローセルチェックとRun開始時のポア数は、約10%程度の変動が起こります。シークエンシング開始時に報告されたポアの数が大幅に減少している場合は、ライブラリー中の汚染物質がメンブレンを損傷していたり、ポアをブロックしている可能性があります。インプット材料の純度を向上させるために、別のDNA/RNA抽出または精製方法が必要となる場合があります。コンタミネーションの影響は、Contaminants Know-how pieceを参照にして下さい。夾雑物を除去するために別の抽出方法extraction method をお試しください。 |
MinKNOWのスクリプトに問題
| 問題点 | この問題が生じた可能性のある原因 | 解決策とコメント |
|---|---|---|
| MinKNOW に 「Script failed」と表示されている" | コンピューターを再起動し、MinKNOWを再起動します。問題が解決しない場合は MinKNOW log files MinKNOWログファイルを収集し 、テクニカルサポートにご連絡ください。他のシークエンシングデバイスをお持ちでない場合は、 フローセルとロードしたライブラリーを4℃で保管することをお勧めします。詳細な保管方法については、テクニカルサポートにお問い合わせください。 |
ポア占有率が40%未満
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
| ポアの占有率が40%以下 | フローセルに十分なライブラリーがロードされていなかった。 | シークエンシングライブラリーを正確に濃度測定し、適切な容量がフローセルにロードされていることを確認してください(詳しくはそれぞれのプロトコールをご覧ください)。 ロードする前にライブラリーを定量し、 Promega Biomath Calculatorなどのツールを使用してfmolを計算してください。[dsDNA: µ g to fmol]を選択してください。 |
| ポア占有率が0に近い | Ligation Sequencing Kitを使用したが、シークエンシングアダプターはDNAにライゲーションしなかった。 | シークエンシングアダプターのライゲーションステップでは、必ずNEBNext Quick Ligation Module(E6056)とOxford Nanopore Technologies Ligation Buffer(LNB、シークエンスキットに付属されています。)を使用し、各試薬の量を適切に使用してください。サードパーティ試薬の完全性をテストするために、Lambdaのコントロールライブラリーを調製することもできます。 |
| ポア占有率が0に近い | シークエンシングアダプターライゲーション後の洗浄工程で、LFBまたはSFBの代わりにエタノールを使用してしまった。 | エタノールはシークエンシングアダプター上のモータータンパク質を変性させる可能性があります。シークエンシングアダプターのライゲーション後にLFBまたはSFBバッファーを使用したことを確認して下さい。 |
| ポア占有率が0に近い | フローセルにテザーがない | テザーはフローセルのプライミング時に追加されます(キット9、10、11はFLTチューブ、キット14はFTUを使用。ウルトラロングのDNAキットにはFTUを使用。) プライミングの前に、FLT/FCT/FTUがバッファー(キット9、10、11はFB、キット14はFCF)に添加されていることを確認してください。 |
予想より短いリード長
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
| 予想より短いリード長 | DNAサンプルの不要な断片化 | 読み取り長はサンプルDNA断片の長さを反映します。サンプルDNAは、抽出およびライブラリー調製中の操作で断片化した可能性があります。 1. 抽出の最適な方法については、Extraction Methods の抽出方法を参照してください。 2. ライブラリー調製に進む前に、アガロースゲル電気泳動で、サンプルDNAのフラグメント長の分布を確認してください。 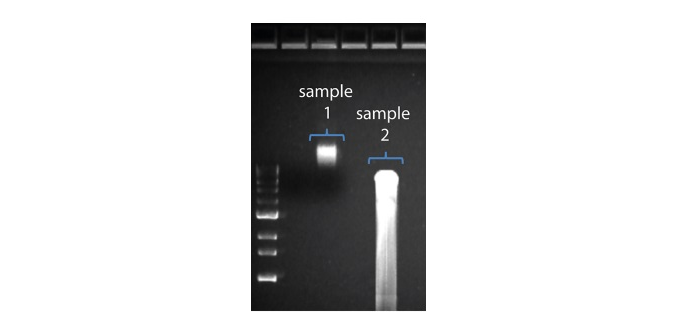 上の画像では、サンプル1は高分子量ですが、サンプル2は断片化されています。 上の画像では、サンプル1は高分子量ですが、サンプル2は断片化されています。3. ライブラリー調製中は、試薬を混合するためのピペッティングやボルテックス操作は、プロトコルで指示がないかぎり行わないでください。 |
利用できないポアの割合が多い場合
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
利用できないポアの割合が大きい(チャンネルパネルとポアのアクティブポートで青く表示されています) 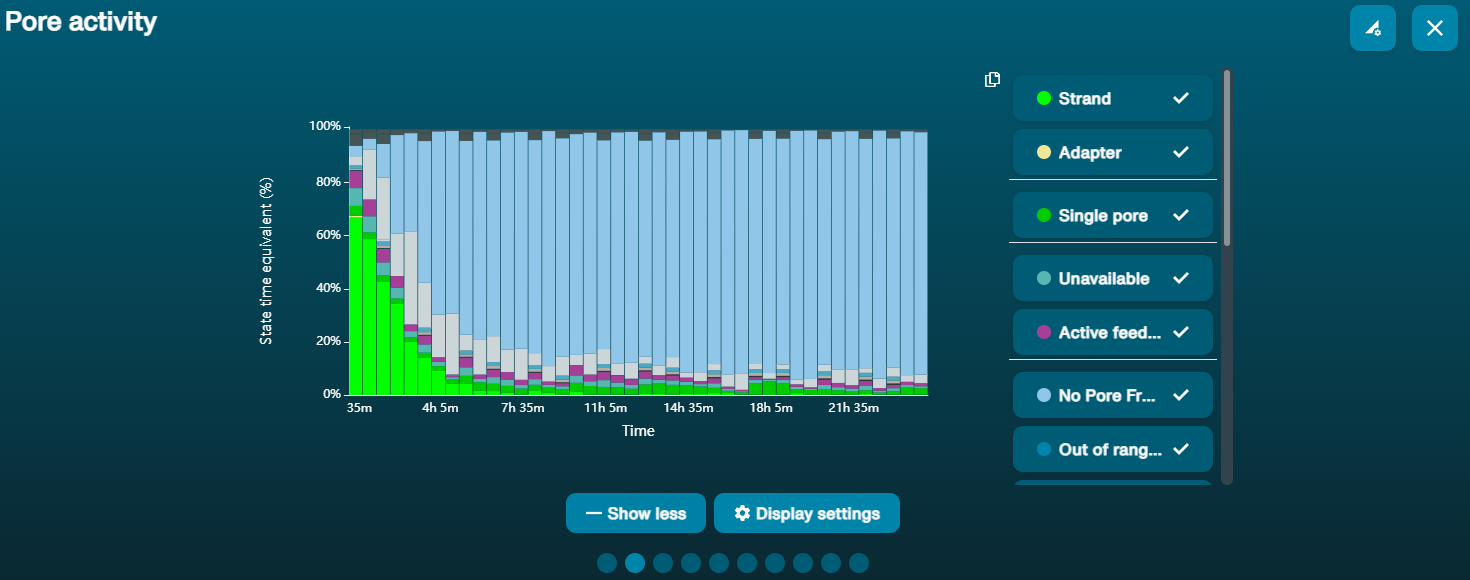 上のアクティブなポアの図は、時間の経過とともに「利用できない」ポアの割合が増加していることを示しています。 上のアクティブなポアの図は、時間の経過とともに「利用できない」ポアの割合が増加していることを示しています。 | サンプル内に不純物が含まれている | 一部のポアに吸着する不純物は、MinKNOWに組み込まれたポアのブロック解除機能によって、ポアから除去することができます。 このステップが完了すると、ポアの状態が「sequencing pore」に戻ります。利用できないポアの部分が多いか、増加した場合: 1.Flow Cell Wash Kit nuclease flush using the Flow Cell Wash Kit (EXP-WSH004) を用いて、ヌクレアーゼ洗浄を 行うことができます。又は 2. PCRを数サイクル実行してサンプルDNAの量を増やし、サンプルDNAに含まれる問題の不純物が相対的に減る(希釈される)ようにします。 |
Inactiveのポアの割合が高い
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
| 利用できない(inactive/unavailable)ポアの割合が高い(チャネルパネルとポアアクティブポートでは水色で表示されています)ポアまたは膜に損傷が起きてしまった。 | 気泡がフローセルに混入した。 | フローセルのプライミングやライブラリーのロードで気泡が入ると、ポアに不可逆的なダメージを与える可能性があります。 推奨の操作方法については、Priming and loading your flow cell のビデオをご覧ください。 |
| 利用できないポアの割合が多い場合 | サンプルDNAに含まれる不純物 | 既知の化合物問題で、サンプルDNAに多糖類が含まれた事で、植物のゲノムDNAと結合しポアをブロックした。 1. 植物葉DNA抽出法 Plant leaf DNA extraction methodをご参照ください。 2. QIAGEN PowerClean Pro キットを使用してクリーンアップして下さい。 3. QIAGEN REPLI-g kit.キットを使用して、元のgDNAサンプルで全ゲノム増幅を実行します。 |
| 利用できないポアの割合が多い場合 | サンプル内に不純物が含まれている | 不純物の影響は、 Contaminants の ノウハウを参照して下さい。 サンプルDNAに不純物を残留させないために別の抽出方法をお試しください。 |
温度変動
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
| 温度変動 | フローセルとデバイスの接続が途切れている。 | フローセルの背面にある金属プレートを覆っているヒートパッドがあることを確認してください。 フローセルを再度挿入し、コネクターピンがデバイスにしっかりと接触していることを確認するために軽く押してください。問題が解決しない場合は、テクニカルサービスにご連絡してください。 |
目標温度に到達しない場合
| 問題点 | 予想される原因 | 解決策とコメント |
|---|---|---|
| MinKNOWが "Failed to reach target temperature "(目標温度に達しなかった)と表示する。" | 装置が通常の室温より低い場所、または風通しの悪い場所(排気が出来ない場所)に置かれた時にフローセルが過熱してします。 | MinKNOWでは、フローセルが目標温度に到達するまでの既定の時間枠があります。時間枠を超えると、エラーメッセージが表示され、シークエンシング実験が続行されます。しかし、不適切な温度でシークエンスを行うと、スループットが低下し、qスコアが低下する可能性があります。シークエンシングデバイスが風通しの良い室温に置かれていることを確認して、MinKNOW再スタートしてください。MinION Mk 1Bの温度制御の詳細については、FAQ を参照してください。 |







